利用MapQTL6进行QTL定位分析
MapQTL6是和Joinmap同一家的软件,利用的输入文件也是可以从Joinmap结果中获得。
MapQTL6主要的输入文件有三个,分别是以.map,.loc和 .qua结尾的文件

这几个文件都可以用Notepad++打开和修改
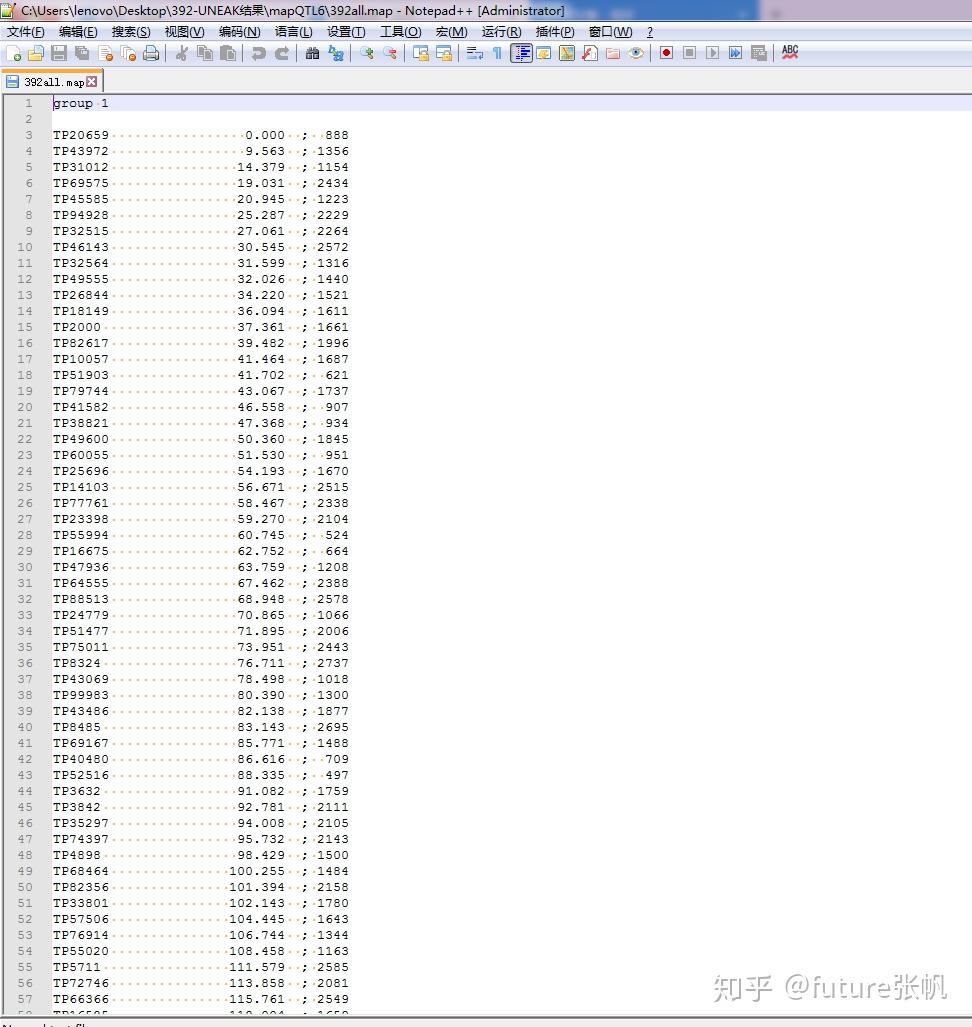
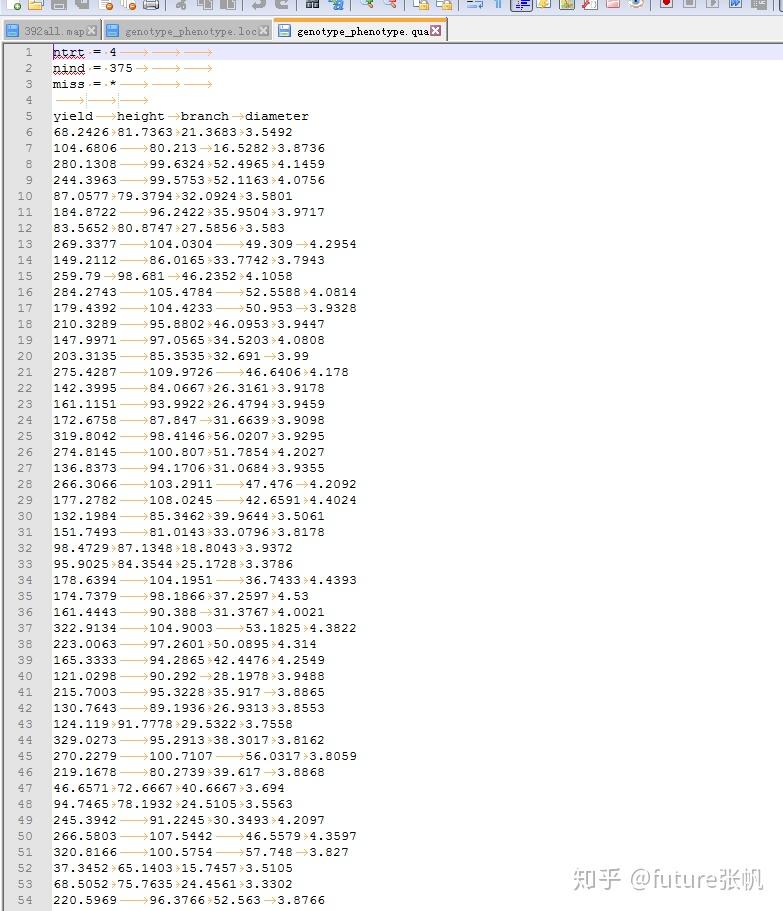
1 第一个文件是392all.map,这个文件是连锁图信息,可以从joinmap的loc文件中获得
joinmap结果文件中的loc文件
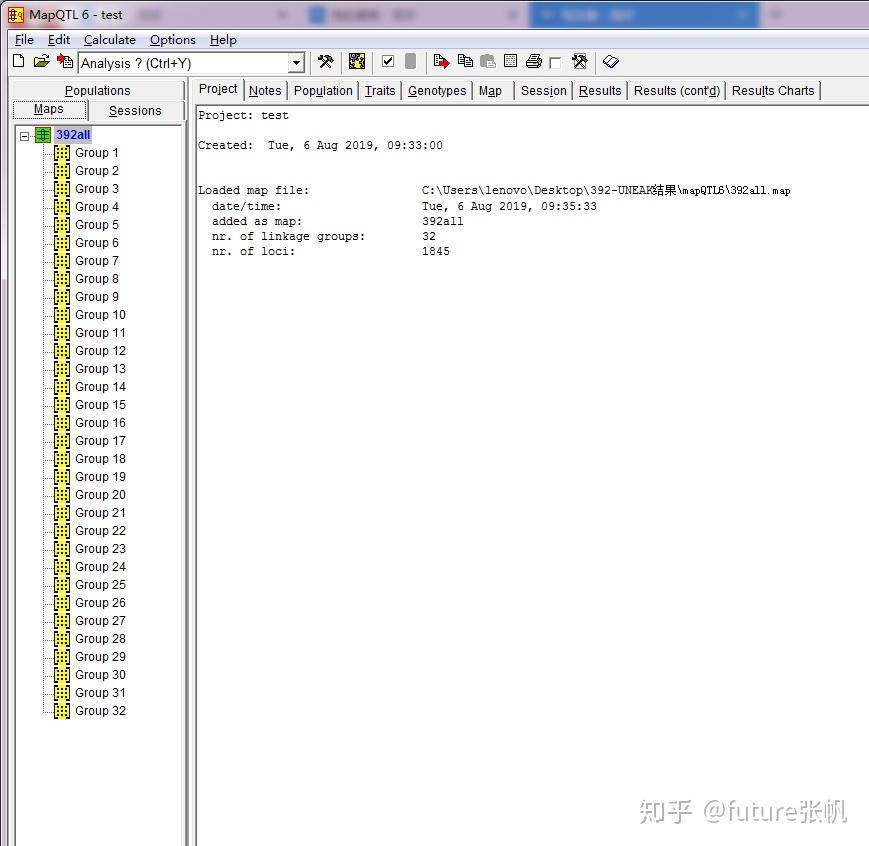
392all.map数据结果
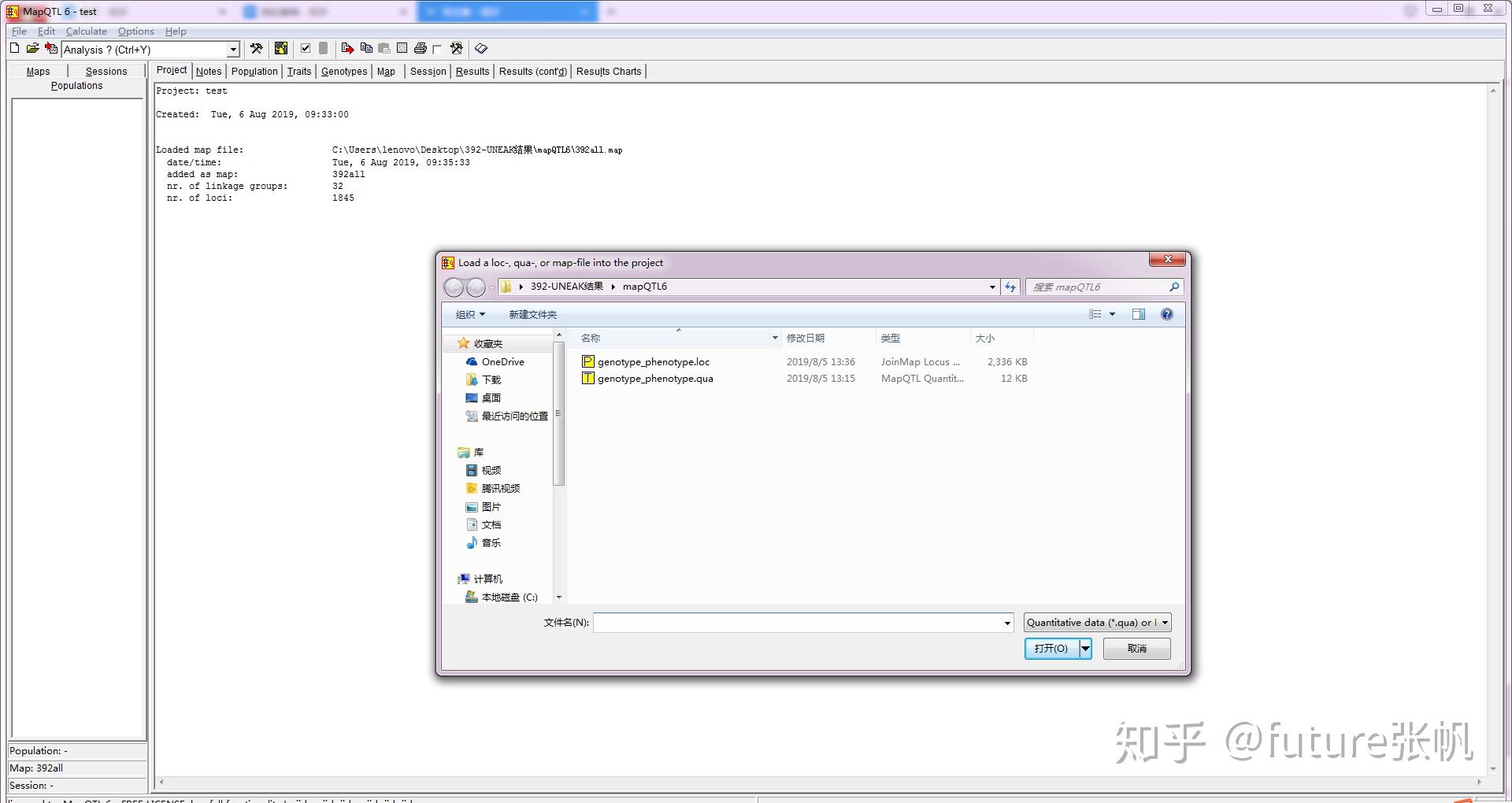
2 genotype_phenotype.loc文件和genotype_phenotype.qua文件,分别存储标记信息和表型信息,这两个文件要名字一样,要不然后面会出错
joinmap结果中有一个是.loc文件,里面存储了所需的基因型信息,找出来,然后重命名就好
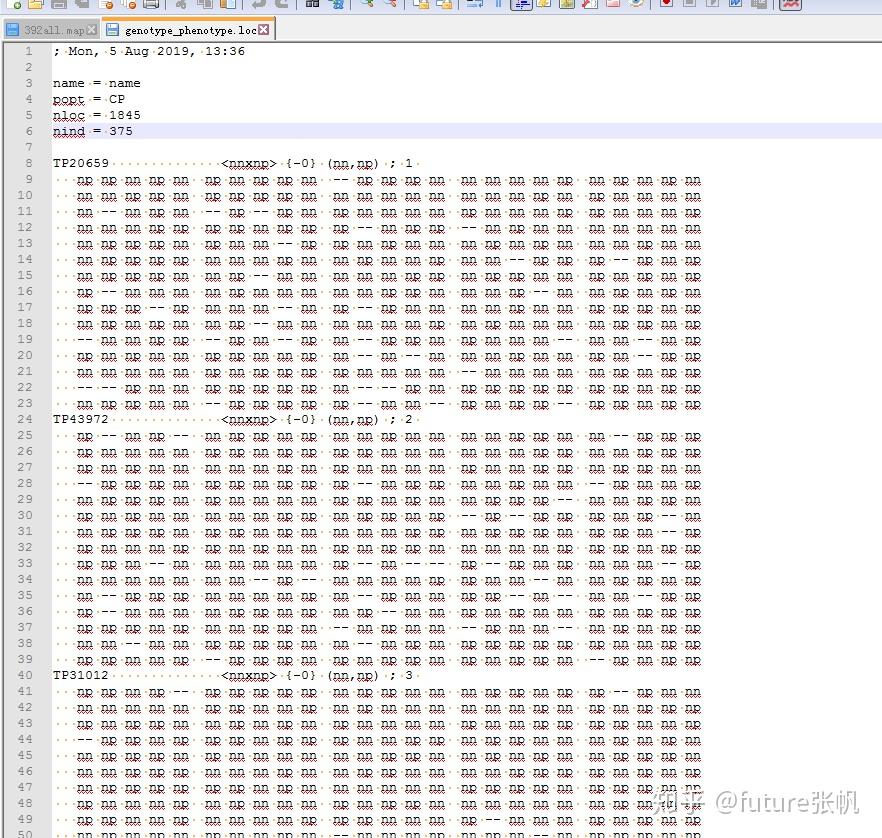
表型信息用EXCEL输入后,保存成制表符分割的txt文件就好,别的格式可能会出错
3 三个文件准备好就可以导入MapQTL6中进行分析了
基本界面
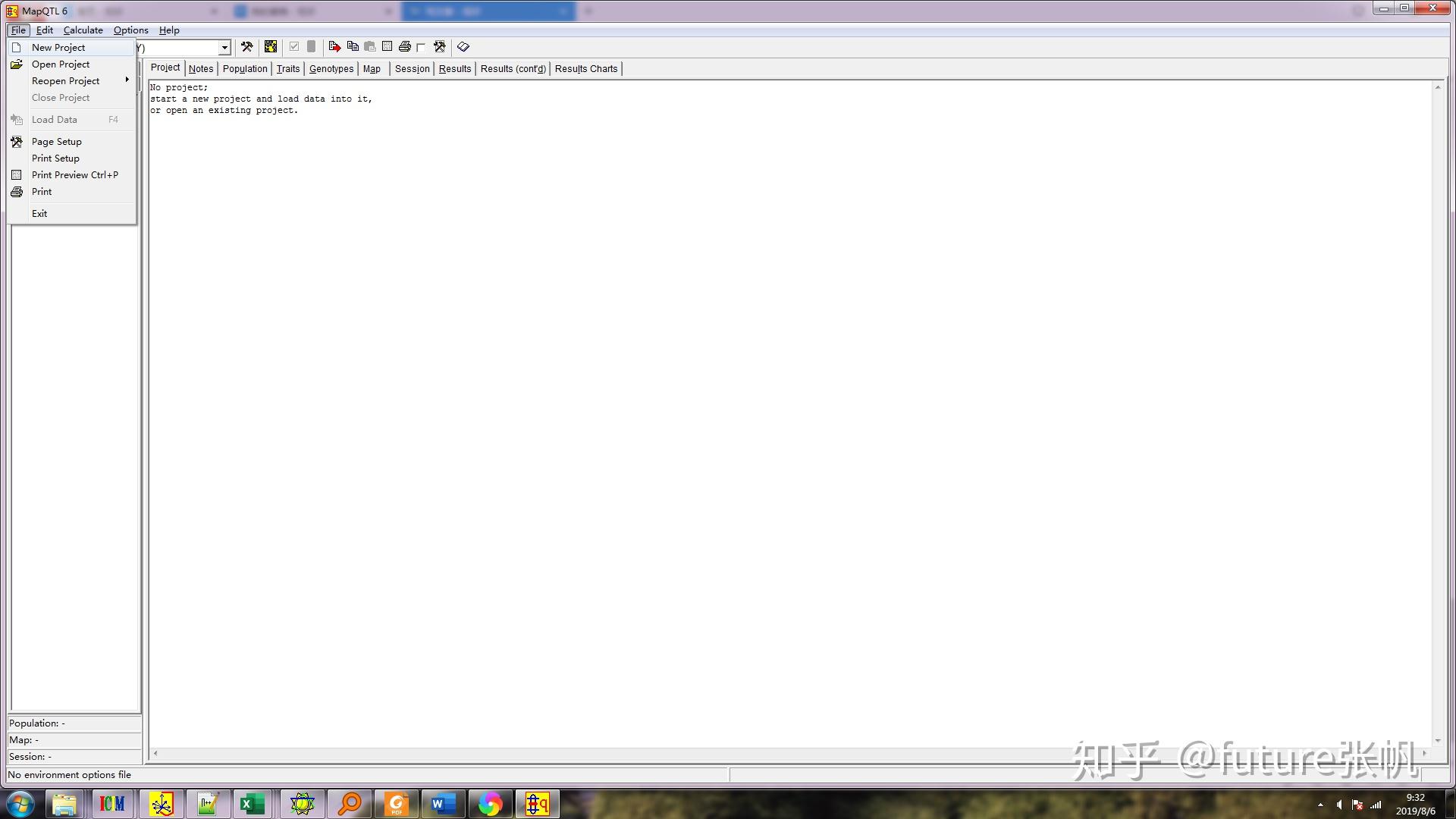
新建一个项目,file→new project
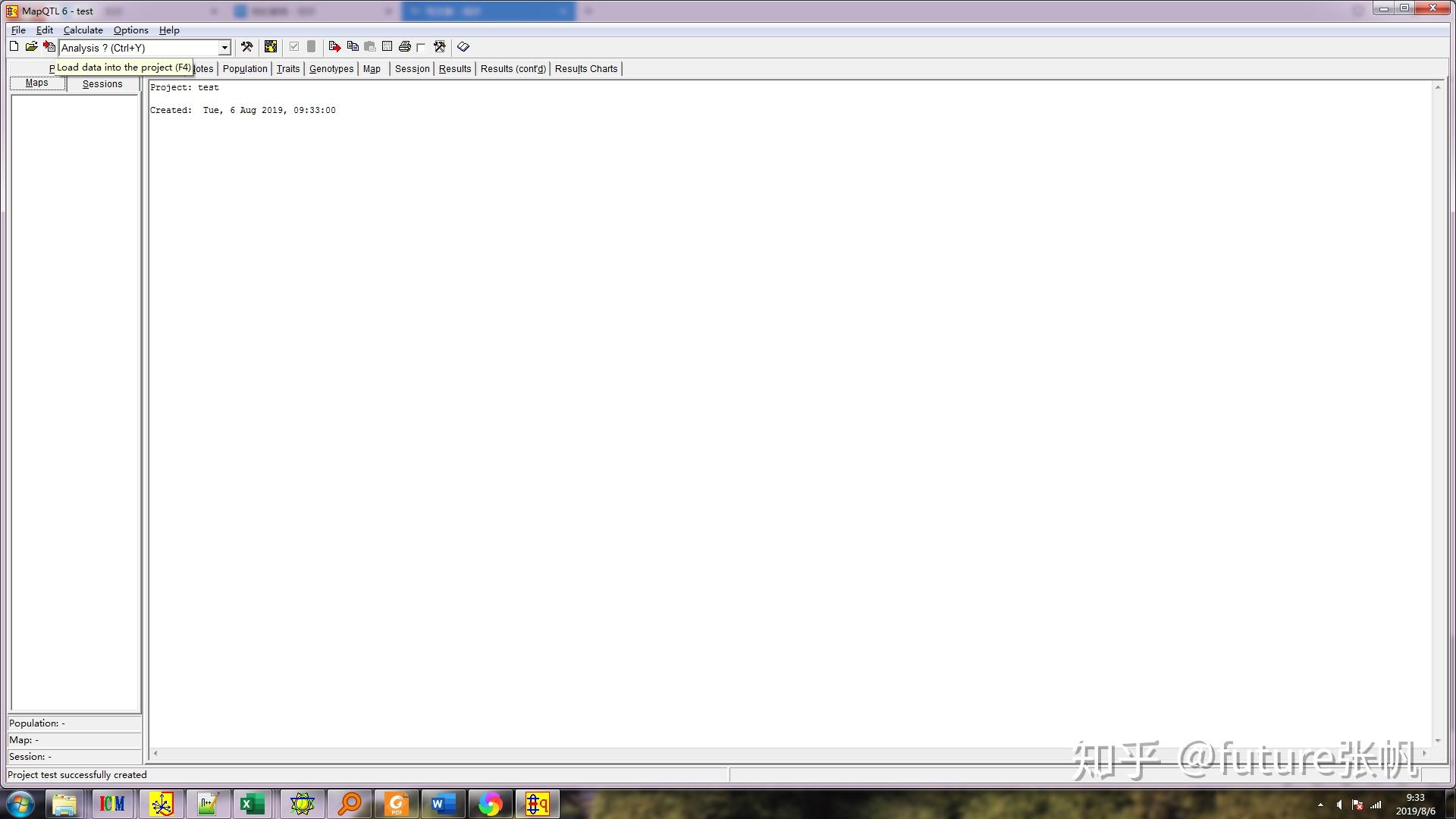
3.1 导入map文件,将鼠标点到map的标签,然后点击load data into the project
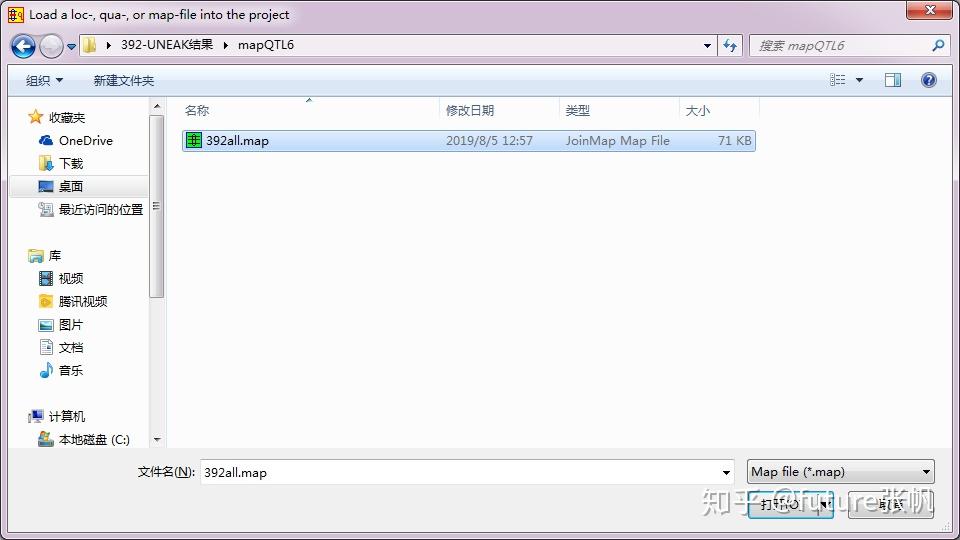
结果:
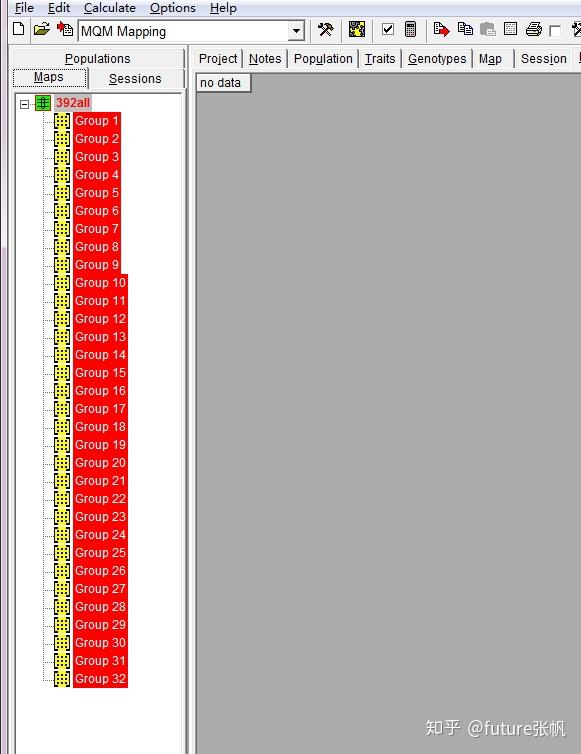
然后右键392all,让所有连锁群变红
3.2 导入.loc文件和.qua文件,将鼠标点到map旁边的populations部分,然后导入数据

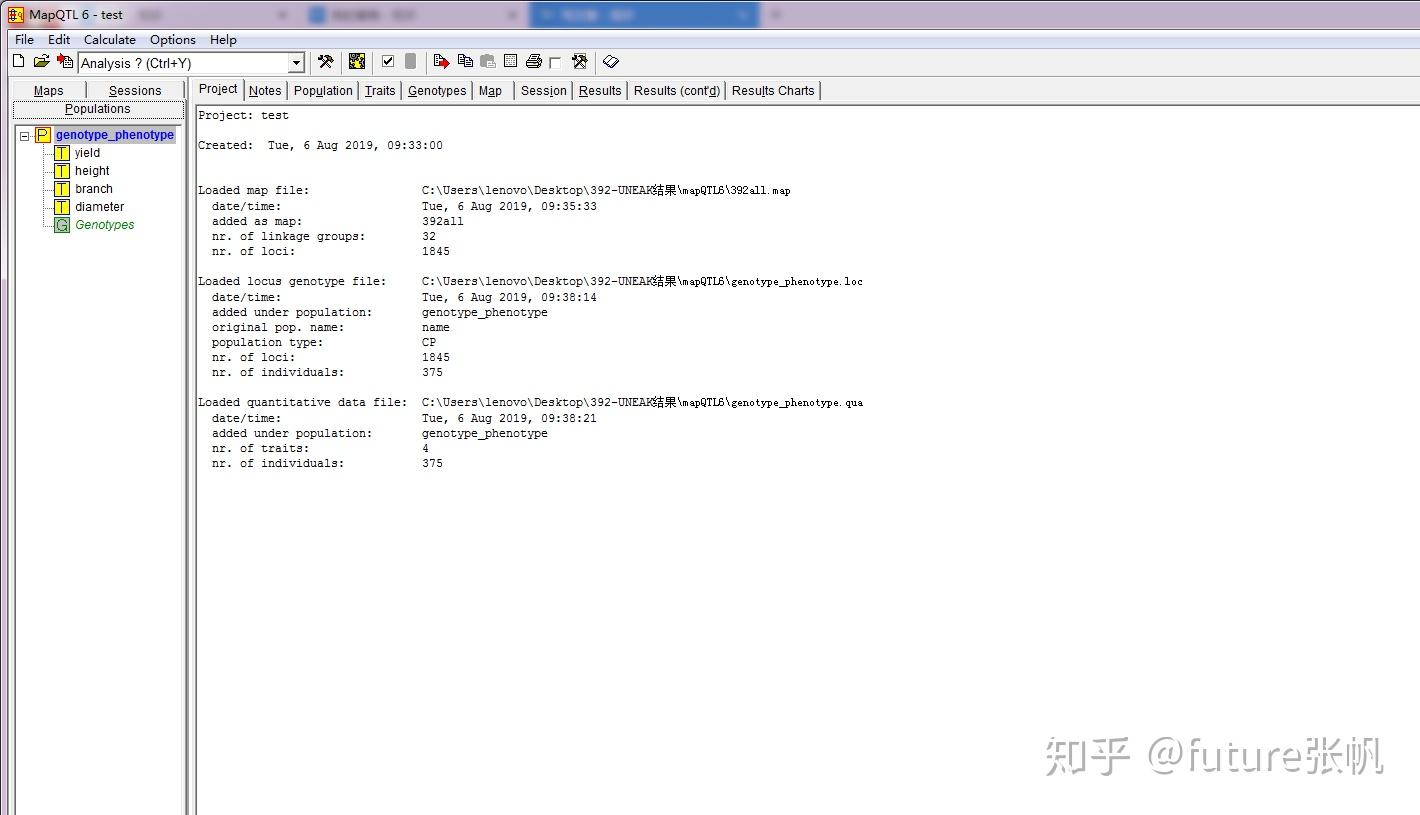
3.3 QTL分析
这个下拉框里面有很多分析方法,这里选择MQM方法
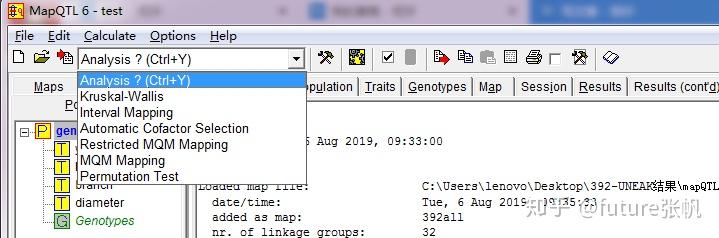
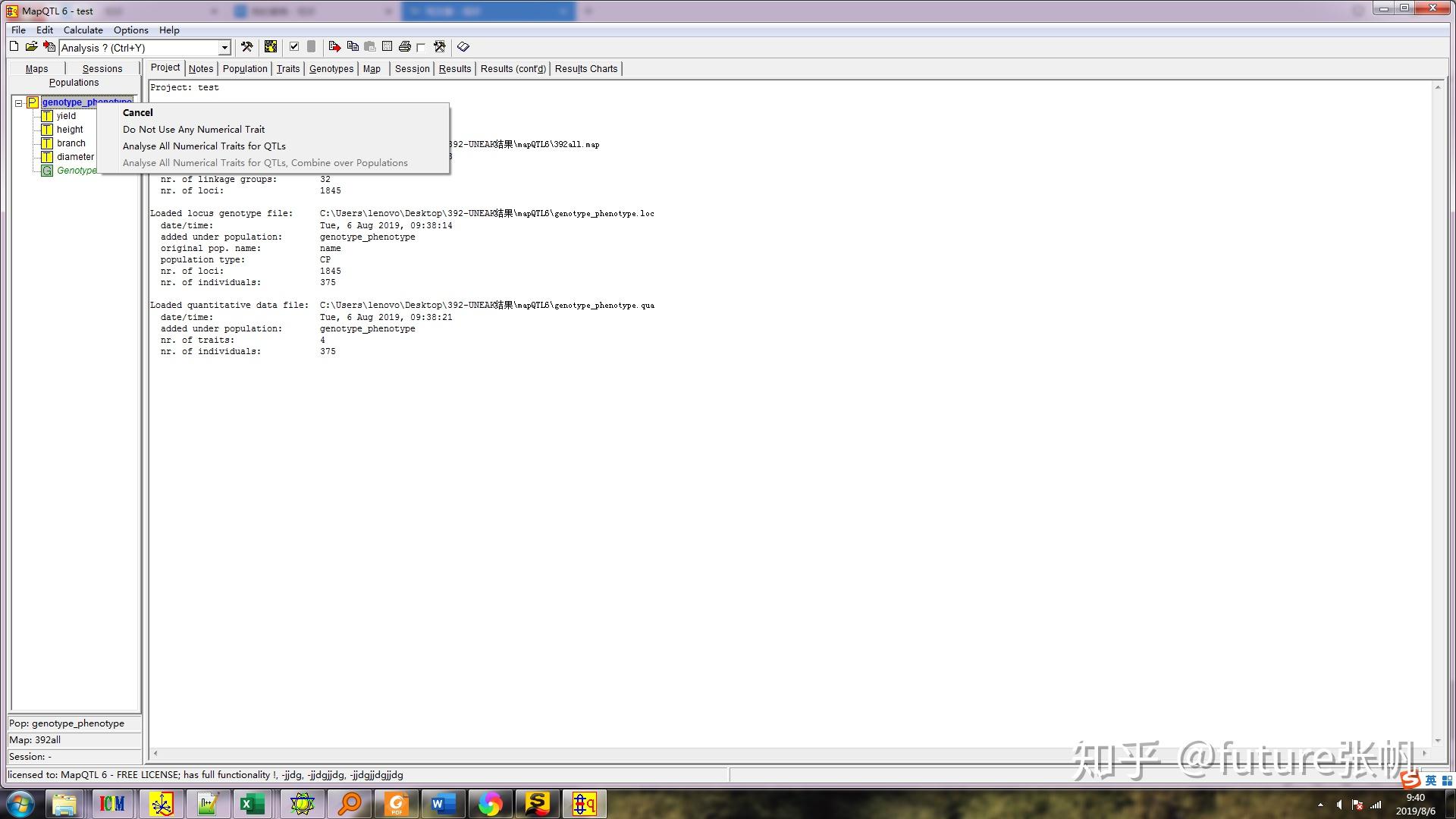
右键genotye_phenotype,然后点击analysis all numerical traits for QTLs

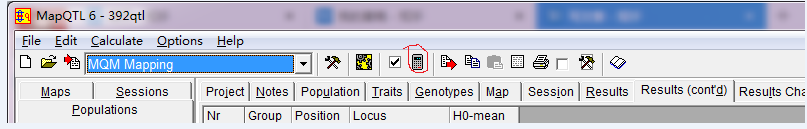
准备工作做好之后,上方有个计算器的图标会变成可点击状态,这时候点一下就开始QTL分析
3.4 结果展示,将鼠标点到sessions上,然后会显示不同表型的分析结果

resuts部分会显示表格形式的结果
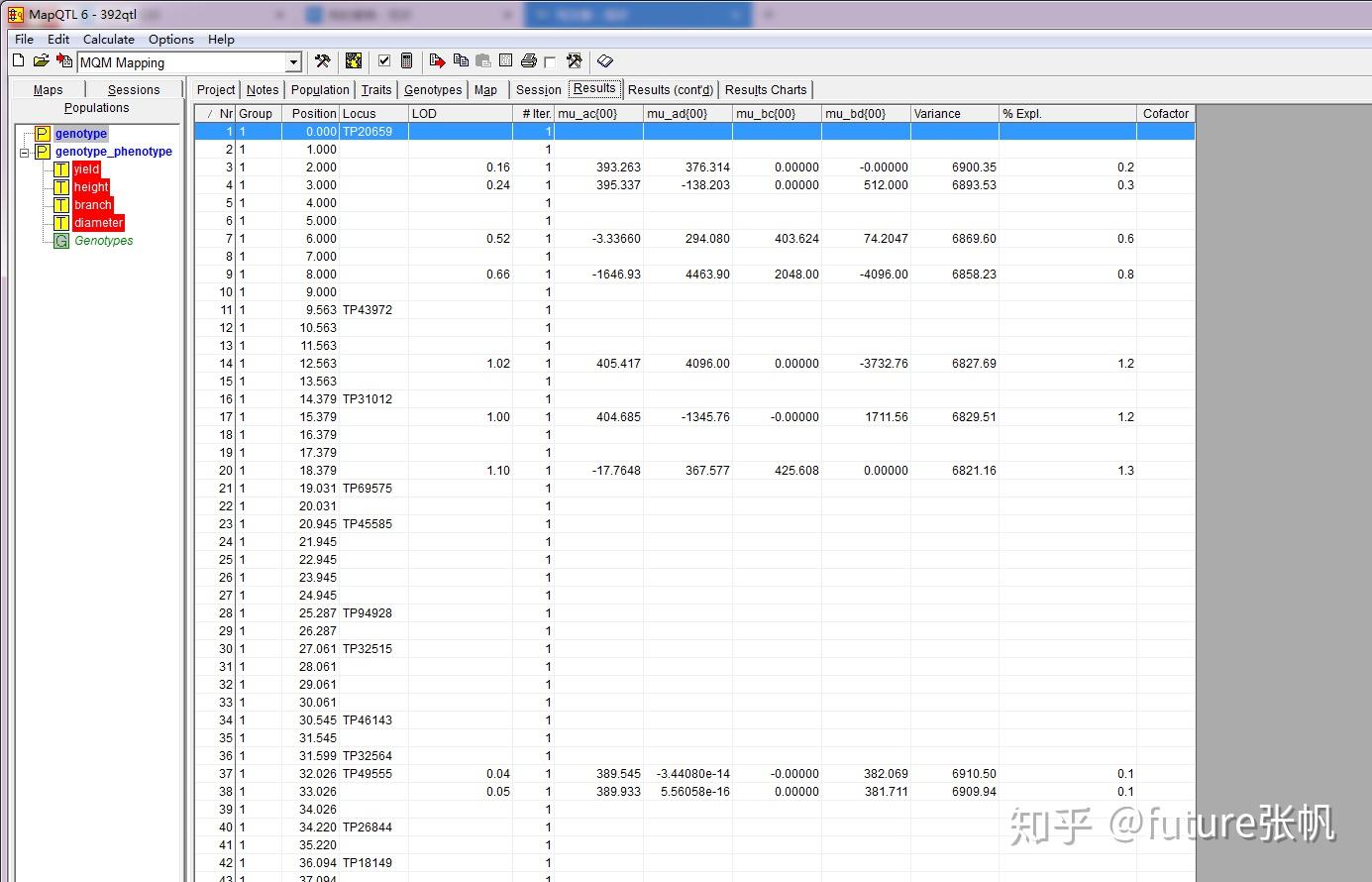
另外也可保存为.txt格式文件
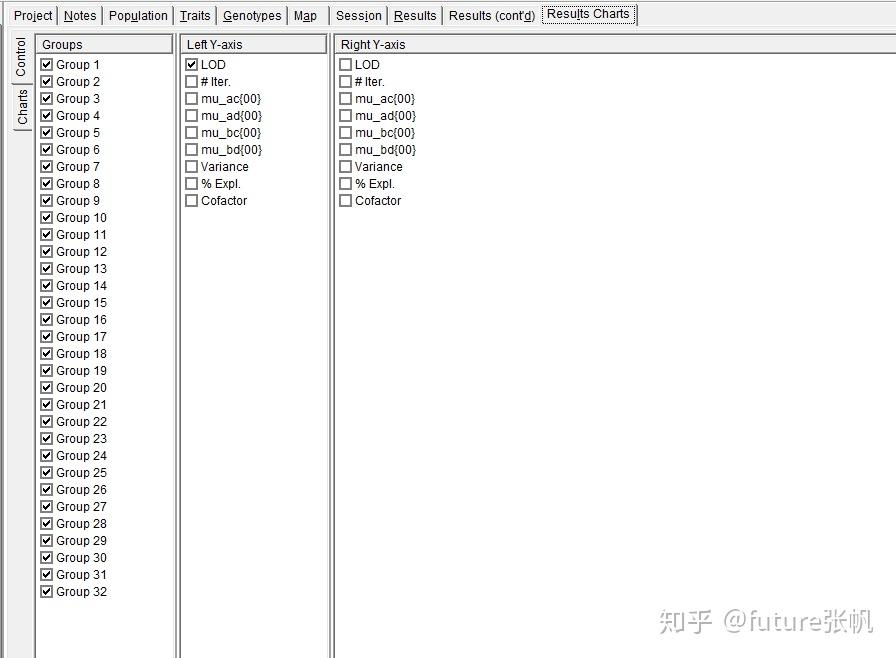
result charts这块能够看图形结果,注意左侧竖向的标签,点击charts

3.5 QTL结果筛选
将.txt格式的文件用excel打开
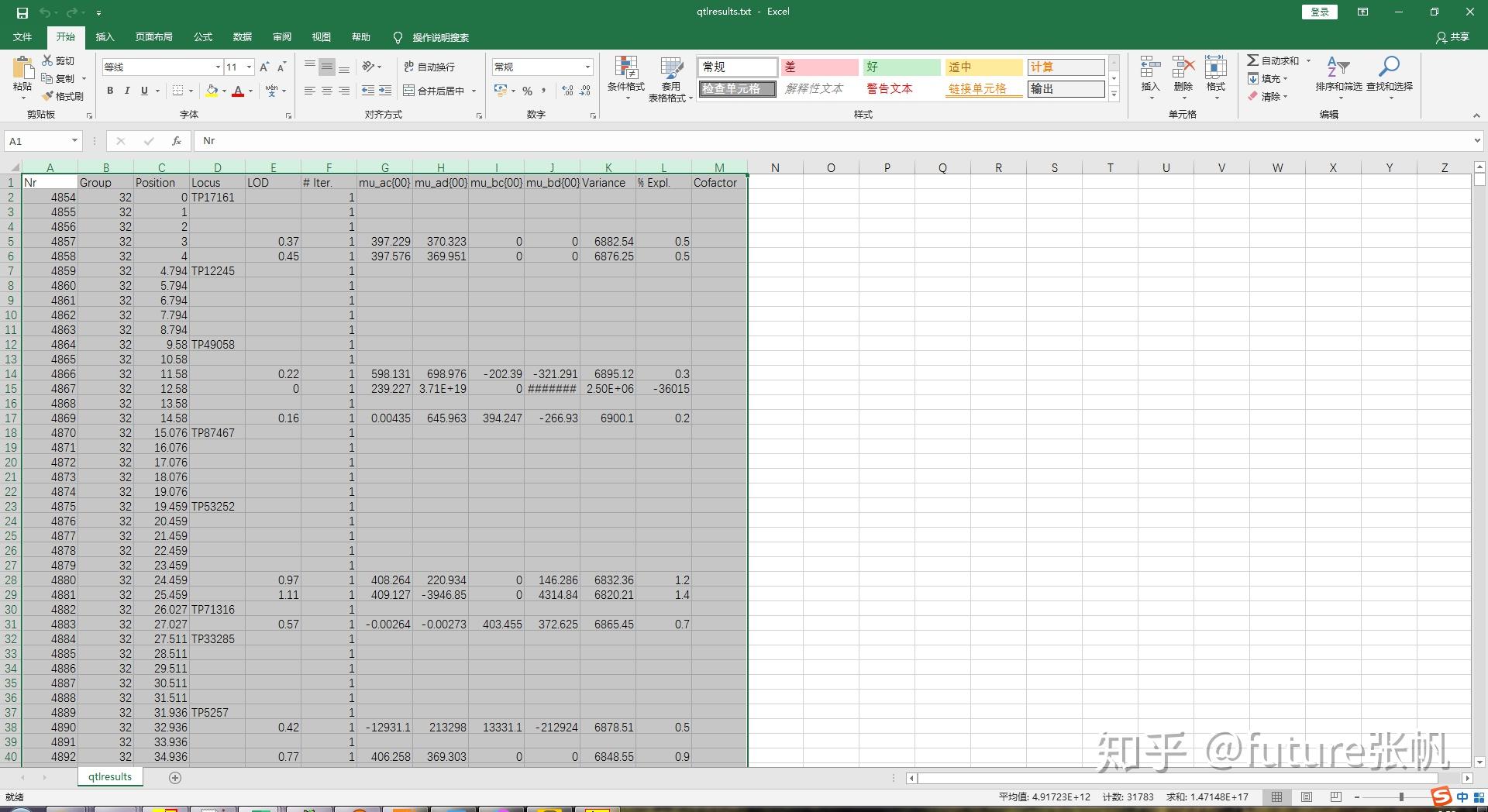
然后选择筛选→LOD→大于3
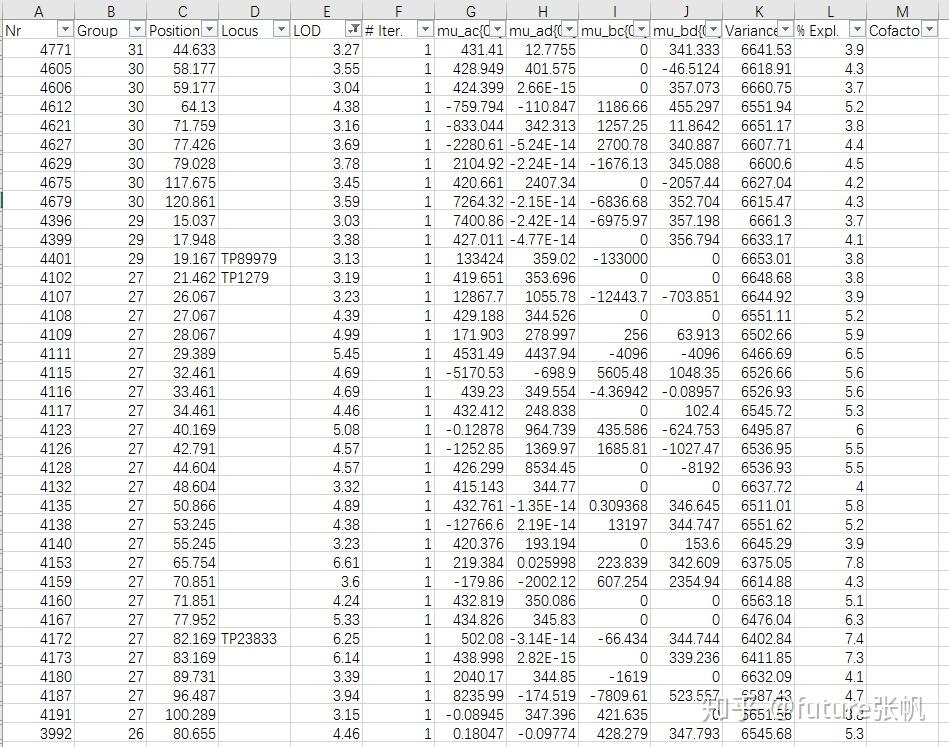
得到的结果:
locus那块有标记,代表这里是有真实标记,如果没有标记,代表的是模拟出的标记。最后可以根据最大LOD-1的值确定QTL区间
总结:
这个软件最费事的是准备数据,需要准备三个文件,最好是在notepad++中修改和保存,这样比较方便,也不容易出问题。
